Curso de RNA-sequencing y análisis de expresión diferencial

Dr. Hober Nelson Núñez Martínez
Universidad Nacional Autónoma de México
Curso de RNA-sequencing y análisis de expresión diferencial

Modalidad en video a tu ritmo
Acceso durante 1 año
10 horas totales
$630.00 MXN ($30 USD)
Información general
En este curso aprenderás los fundamentos, la metodología y las herramientas para el análisis de secuenciación de transcriptomas (RNA-seq). Durante el curso, explorarás los conceptos clave del RNA-seq y desarrollarás las habilidades prácticas para el análisis e interpretación de los datos utilizando datos públicos a tu tiempo y ritmo.
Qué aprenderás
A quién va dirigido este curso
Este curso está dirigido a estudiantes, profesionales e investigadores de las áreas biológicas y de la salud interesados en el aprendizaje del fundamento y la aplicación de las herramientas computacionales para el análisis e interpretación de datos de ensayos de secuenciación de ARN (RNA-seq) en diversos contextos biológicos.
Beneficios del curso
Certificado de finalización
Constancia de
finalización del curso
y realización de un
proyecto con valor
curricular
Instructores expertos
Aprende directamente de expertos del área de las mejores instituciones de Latinoamérica y el mundo
Temario
Módulo 1: Fundamento del ensayo de RNA-seq
- Ensayo de RNA-seq: aplicaciones, ventajas y desventajas.
- Preparación de librerías y secuenciación masiva para el ensayo de RNA-seq.
- Datos de secuenciación masiva: archivos fastq y sus características.
- Análisis de repositorios de datos: Datos públicos
- Práctica 1: Obtención de una cuenta en Galaxy.
Módulo 2: Herramientas para el análisis de datos de RNA-seq
- Flujo de trabajo: importación, calidad, mapeo, análisis de expresión diferencial y visualización.
- Identificación de datos públicos.
- Práctica 2: Importación de datos a Galaxy.
- Práctica 3: Instalación de R y RStudio.
Módulo 3: Flujo de trabajo: calidad, alineamiento y cuantificación
- Análisis de calidad con fastQC y multiQC.
- Alineamiento de las lecturas a un genoma de referencia con STAR.
- Práctica 4: Análisis de calidad del alineamiento.
- Práctica 5: Obtención de conteos en modelos génicos con featureCounts.
- Práctica 6: Análisis de calidad de los conteos.
Módulo 4: Análisis de expresión diferencial
- Normalización y análisis de expresión diferencial con edgeR.
- Filtrado y obtención de genes diferencialmente expresados con R.
- Práctica 7: Conversión de lecturas alineadas a señal con deepTools2.
Módulo 5: Visualización de los datos
- Práctica 8: Gráfico de volcán (volcanoplot).
- Práctica 9: Gráfico de magnitud vs distribución (MD plot).
- Práctica10: Mapa de calor (heatmap).
- Anotación funcional mediante ontología génica.
- Práctica 11: Visualización con el USCS Genome Browser.
Proyecto
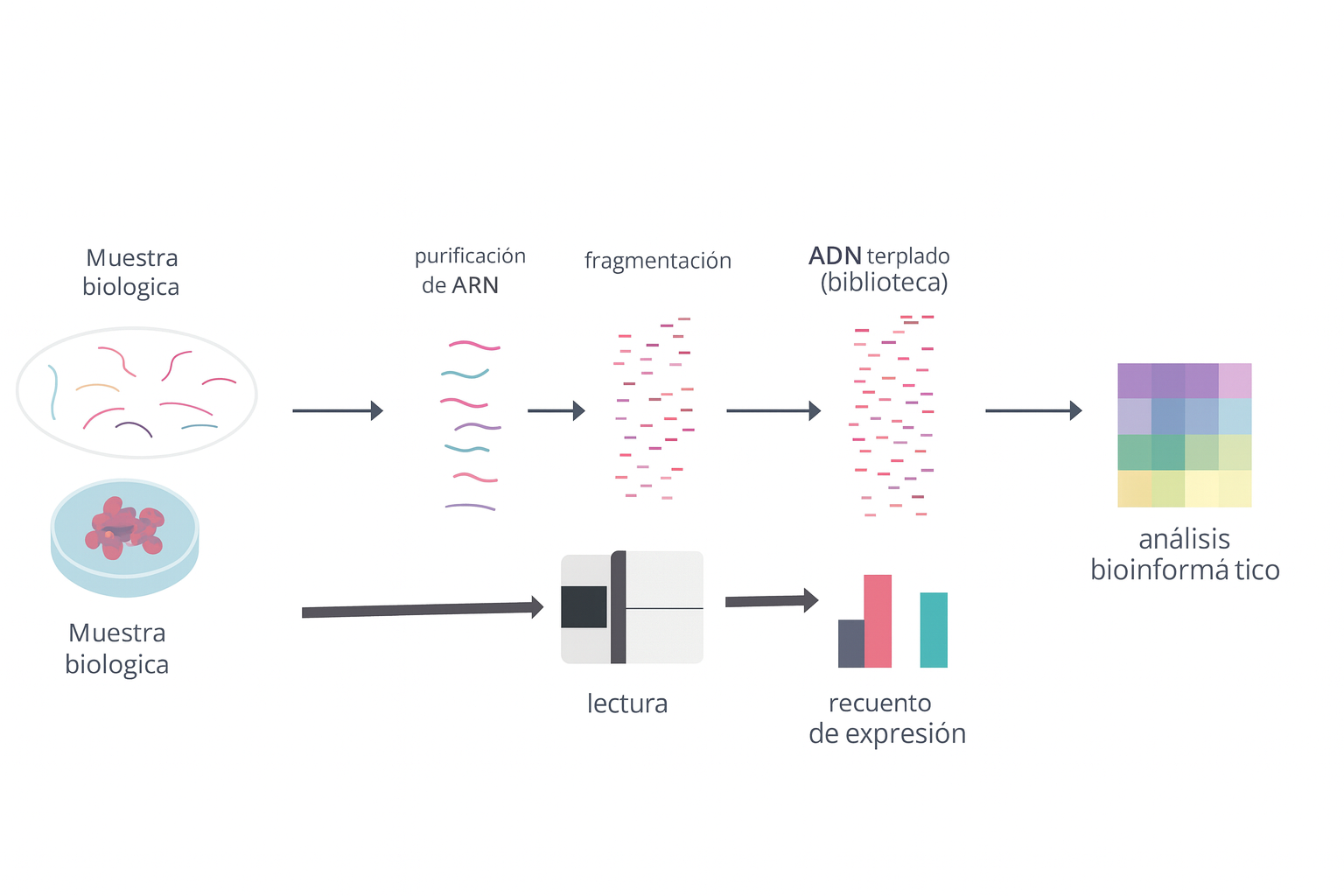
Identificación de genes diferencialmente expresados en un modelo de diferenciación celular
Utilizando datos públicos de RNA-seq y las herramientas para el procesamiento de datos de secuenciación masiva, se identificarán y visualizarán genes diferencialmente expresados con relevancia biológica en la diferenciación celular.
Instructor

Dr. Hober Nelson Núñez Martínez
Universidad Nacional Autónoma de México
Doctor en Ciencias Biomédicas. Ha participado en la aplicación de metodologías experimentales y computacionales en diversos contextos biológicos. Actualmente se especializa en la aplicación de herramientas ómicas y de edición genética para el estudio de los mecanismos regulatorios que influyen en los patrones de expresión génica durante la diferenciación celular.
Certificado digital

Obtendrás un certificado con valor curricular, el cual queda registrado dentro de la plataforma de Conociverso y podrás consultar en cualquier momento para su validación.
Requerimientos técnicos
- Memoria RAM de 8 GB o superior.
Preguntas frecuentes
¿Se entrega un certificado al finalizar este curso?
Sí. Al terminar el curso recibirás un certificado con valor curricular, emitido por Conociverso, que demuestra las habilidades adquiridas durante el curso.
¿Debo tener algún grado académico específico para inscribirme?
No necesariamente. Recomendamos contar con conocimientos básicos en ciencias biológicas, pero el programa está pensado para adaptarse tanto a estudiantes como a profesionales.
¿Necesito tener instalado algún software antes de iniciar?
No. Durante el diplomado aprenderás a instalar y utilizar cada herramienta paso a paso, con la guía de tus profesores. Únicamente necesitas contar con una computadora con al menos 8 GB de RAM.
Si las clases en vivo ya pasaron, ¿aun así puedo tomar este curso?
¡Por supuesto! Todos nuestros cursos están diseñados para que también los puedas realizar en modalidad asincrónica, a tu propio ritmo y en el horario que mejor se adapte a ti. Tendrás acceso a las grabaciones de todas las clases del curso y al material complementario.
¿Emiten factura fiscal?
Sí, emitimos factura fiscal únicamente para México. Para solicitarla, ve a la configuración de tu cuenta, en la sección de pagos encontrarás la opción de facturación. Debe solicitarse dentro del mismo mes en que se realizó la compra.
Reseñas
Este curso me sirvió mucho para ampliar mi conocimiento en el manejo de software para investigación, igualmente puede aclarar todas mis dudas durante el curso. También me gustó que los docentes nos hayan apoyado y explicado de manera clara todos los temas.

Dr. Alejandro Pech Burgos
Médico
La atención a los estudiantes fue de primera en disposición y amabilidad tanto de los organizadores como de los profesores. Los profesores son personas con mucha experiencia y que siempre se esforzaron en dar lo mejor de sí para que pudiésemos aprender cada tema.

Dra. Patricia Landa
Docente e investigadora, Universidad Autónoma de Chapingo
Recomiendo a Conociverso son súper profesionales y flexibles. Me encanta su servicio al cliente de alta calidad y formalidad. Los cursos son de alta calidad académica y lo mejor de expertos en el área. Y costos asequibles para los principiantes.

Dra. Victoria Edwina Campos García
Docente e investigadora, UNAM
Las clases son muy dinámicas y todos los profesores son expertos en su tema, muchos de ellos son jóvenes investigadores y eso es un plus de motivación que te da el verlos y aprender de ellos.

M.C. José Adrián Coral Góngora
Profesor de cátedra, CINVESTAV UNIDAD MONTERREY
Me gustó mucho que trabajamos con ejemplos reales. Adquiriendo herramientas aplicables a nuestras líneas de investigación. Los instructores siempre atentos, siempre pendientes de responder dudas. Todo el material disponible, y la posibilidad de revisar la grabación del curso muy bueno para los que nos somos expertos.

Dra. Maria Leticia Arena Ortiz
Profesora investigadora, UNAM
M1 Fundamento del ensayo de RNA-seq
- Desarrollo experimental del ensayo de RNA-seq: preparación de librerías y secuenciación masiva.
- Datos de secuenciación masiva y sus características: archivos fastq y sus características .
- Datos públicos de RNA-seq: repositorios de datos.
- Práctica: obtención de una cuenta en Galaxy.
M2 Herramientas para el análisis de datos de RNA-seq
- Flujo de trabajo para el procesamiento de los datos: importación, calidad, mapeo y análisis de expresión diferencial.
- Práctica: identificación de datos públicos de RNA-seq.
- Práctica: uso de Galaxy para la importación de los datos.
- Práctica: instalación de R y RStudio.
M3 Flujo de trabajo: calidad, alineamiento y cuantificación
- Análisis de calidad de las lecturas de secuenciación: uso de fastQC y multiQC.
- Mapeo de las lecturas a un genoma de referencia: uso de STAR.
- Cuantificación de las lecturas en modelos génicos: uso de FeatureCounts.
M4 Análisis de expresión diferencial
- Análisis de expresión diferencial de genes: uso de edgeR.
- Filtrado y manipulación de los datos procesados: uso de R y RStudio para el filtrado de los datos.
- Conversión de lecturas mapeadas a señal normalizada: uso de deepTools2.
M5 Visualización de los datos
- Práctica: Gráfico de volcán (volcanoplot).
- Práctica: Gráfico de magnitud vs distribución (MD plot).
- Práctica: Mapa de calor (heatmap).
- Anotación funcional mediante ontología génica.
- Práctica: Visualización con el USCS Genome Browser.

Curso de RNA-sequencing y análisis de expresión diferencial

Dr. Hober Nelson Núñez Martínez
Universidad Nacional Autónoma de México
Modalidad en video
Acceso durante 1 año
10 horas totales
Nivel intermedio
$630.00 MXN ($30 USD)
Accede a todos nuestros cursos
Especialízate y mantente actualizado como científico bajo un precio cómodo
Conociverso Lite
Cancela cuando lo necesites-
Acceso a más de 40 cursos
-
Certificados ilimitados
-
Ruta personalizada de aprendizaje
Conociverso Pro
Acceso completo anual-
Accede a más de 40 cursos
-
Certificados ilimitados
-
Ruta personalizada de aprendizaje
-
Cursos exclusivos
Plan institucional
Planes personalizados para organizaciones-
Cursos o planes personalizados
-
Evaluación y métricas de aprendizaje
-
Descuento dependiendo el tamaño de tu organización


